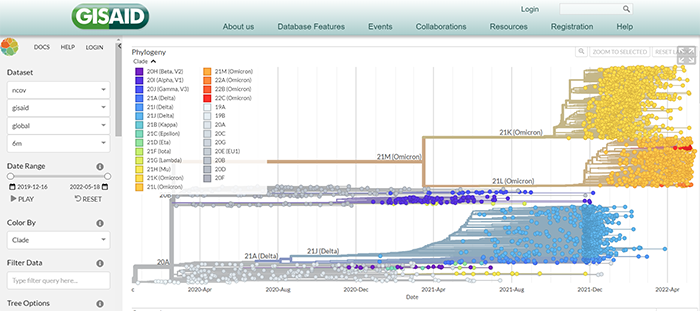

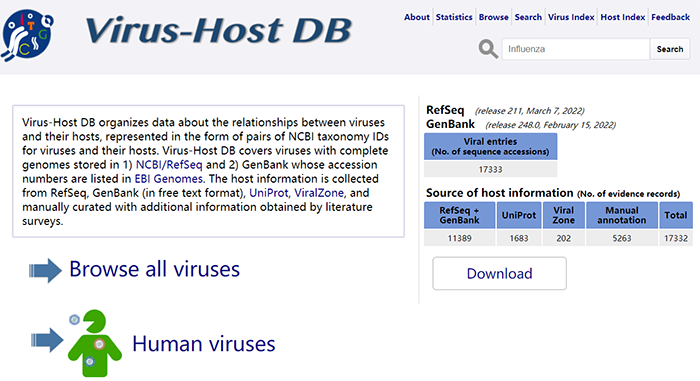
3.Virus-Host DB,链接: https://www.genome.jp/virushostdb/
Virus-Host DB组织有关病毒与其宿主之间关系的数据,以病毒及其宿主的 NCBI分类对应的ID形式。Virus-Host DB涵盖具有完整基因组的病毒,这些病毒存储在①NCBI/RefSeq和②GenBank中,其登录号在EBI Genomes中列出。主机信息是从RefSeq、GenBank、UniProt、ViralZone收集的,并使用通过文献调查获得的附加信息进行手动管理。
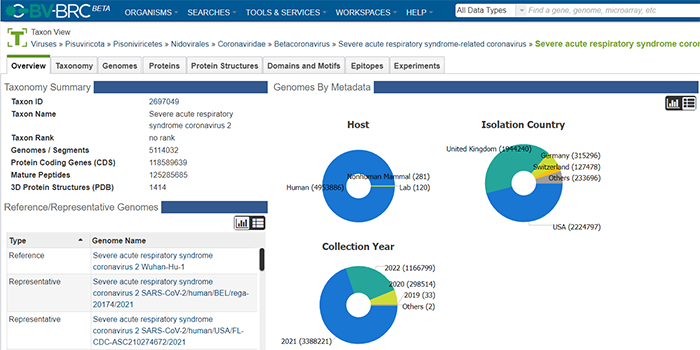
4.BV-BRC,链接: https://www.bv-brc.org/
BV-BRC (Bacterial and Viral Bioinformatics Resource Center,细菌和病毒生物信息学资源中心) 是一个信息系统,旨在通过将病原体信息与丰富的大数据和分析工具相结合,支持生物医学研究界在细菌和病毒传染病方面的工作。BV-BRC结合了来自两个长期运行中心的数据、技术和广泛的用户社区:PATRIC(细菌系统)和 IRD/ViPR(病毒系统)。除了PATRIC中的数十万个细菌基因组和IRD/ViPR中超过一百万个病毒基因组外,这两个资源还包含蛋白结构和功能、临床研究、药物靶点和耐药性、流行病学和其他特征的数据,并提供开放的用于数据分析和基因组注释的源工具。
5.COVdb,链接:https://covdb.stanford.edu/
COVdb可用于SARS-CoV-2 突变分析,可以使用文本输入每个SARS-CoV-2基因、Spike、RdRP、nsp1-10(包括PLpro和3CLpro)、nsp13-16、ORF3a、E、M、ORF6、ORF7a、ORF8、N和ORF10的突变盒。键入或粘贴由一个或多个空格分隔的突变。突变应该以基因名开头,然后是一个冒号。对于Spike蛋白,基因名称和冒号是可选的。参考野生型和分隔逗号是可选的。如果在一个位置有多个氨基酸混合物,写下两个氨基酸(中间的斜线是可选的)。插入用“ins”表示,删除用“del”表示。
6.Reference Viral DataBase (RVDB),网址:https://rvdb.dbi.udel.edu/
RVDB由FDA CBER的Arifa Khan小组开发,用于使用二代测序 (NGS) 技术增强病毒的检测。RVDB以非聚集 (U-) 和聚集 (C-) 核苷酸序列文件的形式提供。生成和更新RVDB涉及的脚本和步骤已被组装到一个管道(在mSphere中报告),并且可以在GitHub 上获得说明。RVDB的蛋白版本由巴斯德研究所的Marc Eloit小组开发(RVDB-prot和RVDB-prot-HMM)。蛋白RVDB可用于补充使用这些核苷酸数据库的分析。

7.Pathogen Databases,链接:https://www.lanl.gov/collaboration/pathogen-database/
该数据库包括很多病毒数据库,如①HIV 和 HCV 数据库包含有关病毒基因序列、免疫表位、耐药性相关突变和疫苗试验的数据;②丙肝病毒数据库,该项目由美国国家过敏症和传染病研究所 (NIAID) 微生物学和传染病部资助。HCV数据库项目从HIV数据库项目衍生而来,有两个数据库,一个序列数据库和一个免疫表位数据库;③HFV/埃博拉数据库,该数据库包含与埃博拉病毒相关的遗传和免疫学数据,包括搜索界面、基因组浏览器、精选的核苷酸和蛋白质序列比对(在属、种和暴发水平上)、T 细胞表位和抗体结合位点的列表和基因组图谱,重要功能域的列表,以及许多基于 Web 的分析工具。
当然,其他病毒数据库,还有很多,我们这里作简要的分享。
8.NCBA Virus:www.ncbi.nlm.nih.gov/labs/virus/vssi/#/
9.Human-Virus Interaction DataBase:http://zzdlab.com/hvidb/
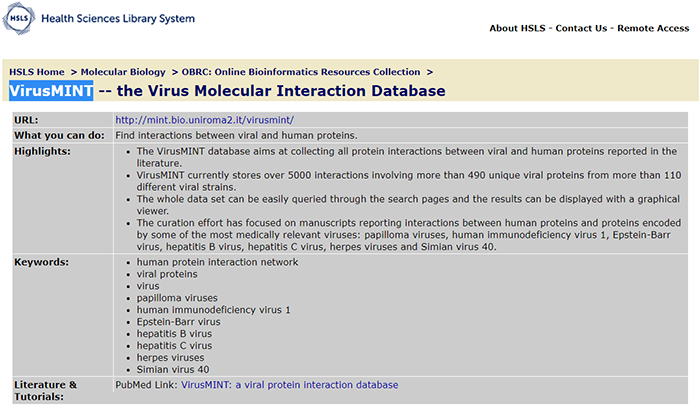
10.VirusMINT:https://www.hsls.pitt.edu/obrc/index.php?page=URL1232734234
11.Virhostome:http://interactome.dfci.harvard.edu/V_hostome/

12.PaVE:https://pave.niaid.nih.gov/

13.ERVd:https://herv.img.cas.cz/
14.COGdb:https://vogdb.org/
15.HPV Sequence Database:http://hpv.unl.edu/HPV/Database.html















