由于下一代测序(NGS)技术的快速发展,近年来基因组数据经历了巨大的增长。因此,用于数据集分析和可视化的软件和工具的数量也在不断增加。目前多数基因组数据分析工具需要编程/脚本语言(R、Python、shell等)的知识和经验,满足软件/硬件需求和解决软件依赖关系,但缺乏图形用户界面(GUI),对于大多数研究人员不太“友好“。
一、GeneCountMerger
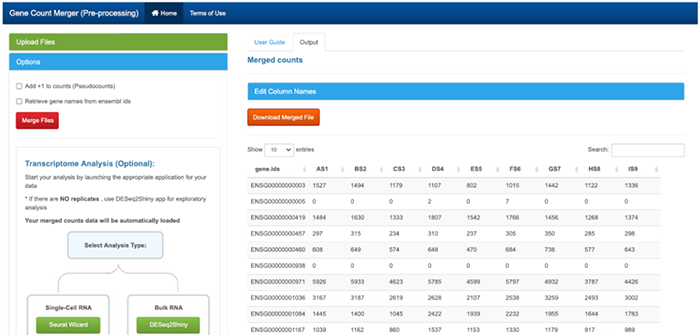
GeneCountMerger主要用于数据的预处理,可以合并单个原始基因计数文件(如htseq-count和featureCounts)。选项包括:
•合并单个样本计数文件到一个矩阵
•合并多个原始计数矩阵
•将Ensembl id转换为基因名
•选择可用基因组
•添加pseudoCounts
•重命名样本名
•下载合并counts文件(csv格式)
•合并转录组分析结果(Seurat Wizard分析单细胞数据;DESeq2Shiny或START分析RNA数据)。
二、Seurat wizards
Seurat wizards使用Seurat包对单细胞RNAseq数据进行质控和分析。允许用户调整可视化中间步骤的输出和状态参数。Seurat wizards相比大多数scRNA-seq分析的web工具,如IS-CellR和SCHNAPPs,使用更为灵活。同时Seurat wizards通过绘制小提琴图检查细胞的分布情况,用户选择相应的截止阀值即可对细胞进行过滤。Elbow/Jackstraw图可以帮助用户在决定是否使用非线性降维。这两种功能都会对后续细胞集群和基因差异分析产生重大影响。
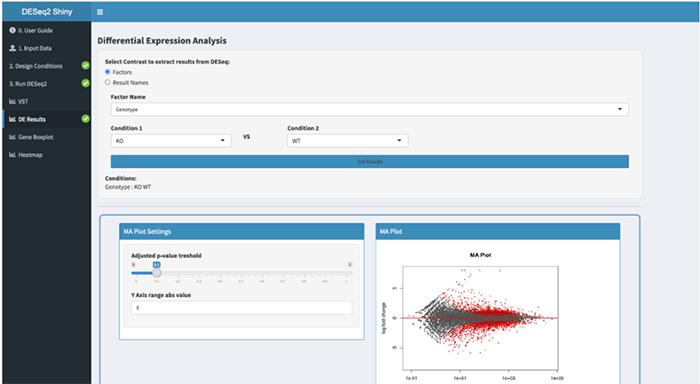
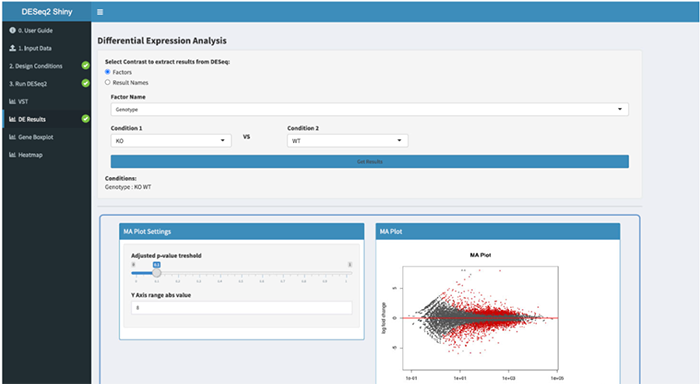
三、DESeq2Shiny
DESeq2Shiny模块封装了DESeq2,用于对RNA-seq数据执行差异表达分析。它提供了数据标准化、转换(用于聚类的rlog和vst转换)以及估计离散度和差异倍数(fold-change)功能。分析结果提供csv格式文件下载,数据可视化包括火山图、热图、密度图、基因表达箱线图和主成分分析图。
四、ClusterProfilerShiny
ClusterProfilerShiny集成了clusterProfiler包,实现了基因组坐标、基因和基因簇的功能的分析和可视化。用户可以使用上游的DESeq2Shiny导入分析数据。允许对GO和KEGG通路进行快速、简单的过表达分析(ORA)和基因集富集分析(GSEA)。分析结果包括点图、词云图、类别网图、基因富集图、GSEA图和KEGG路径图(Pathview包)。